- 複体というのがある
- 単体の集合だ
- お絵かきしてみる
- 単体の隣接行列は、対角成分を0としそれ以外の成分はすべて1であるような行列である
- 複体は単体同士がより小さな単体を共有した形になっている
- したがって、次のようにランダムに作ることができる
- ノード総数を定め
- 複体を構成する「最大化した単体」に属するノード集合を、単体ごとに定め、そのノード集合について全ノードの隣接行列の要素を1にする
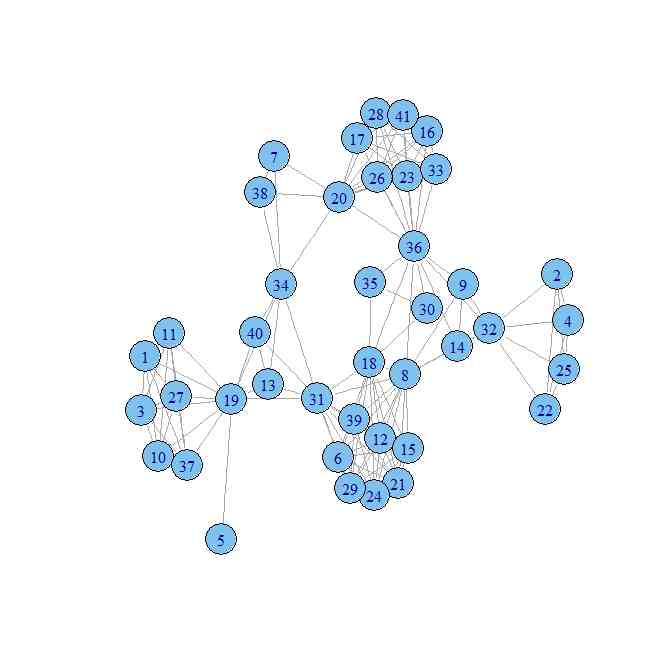
- こうすると、結構、バラバラになった複体ができてしまうので、すべての単体が連結するようにして、「複体っぽさ」を図に表したいときには次のようにすることもできる
- 第1の単体のノード集合を決め、複体に含ませる。以降は、新たな単体を追加するときに、それまでに複体に含まれることになったノードの集合から最低1個のノードは含むようにする
- このようにすると、単体として登録していくときに「単体の最大化」を気にせずにどんどん登録しても、最終的に出来上がる複体の隣接行列には、影響が出ないし、グラフができたあとに、最大化したクリーク(これが複体を構成する最大化した単体に相当する)を抜き出せば、その情報も取れる
- かと思ったが、(1,2),(2,3),(3,1)という3つの1単体の場合と(1,2,3)という1つの2単体の場合が、この処理だと混ざってしまう
library(igraph)
N <- 500
Bs <- list()
max.n <- 10
k <- 10
check <- rep(0,N)
for(i in 1:k){
if(i ==1){
Bs[[i]] <- sample(1:N,sample(1:max.n,1))
}else{
tmp.n <- sample(2:max.n,1)
a <- sample(which(check==1),1)
b <- sample((1:N)[-a],tmp.n-1)
Bs[[i]] <- sort(c(a,b))
}
check[Bs[[i]]]<-1
}
M2 <- matrix(0,N,N)
for(i in 1:length(Bs)){
M2[Bs[[i]],Bs[[i]]] <- 1
}
diag(M2) <- 0
M2 <- M2[which(check==1),which(check==1)]
g2 <- graph.adjacency(M2,mode="undirected")
plot(g2)
maximal.cliques(g2)
n <- 3
r <- c(2,3,4)
R <- prod(r)
m <- list()
m[[1]] <- 0
cnt <- 2
for(i in 1:n){
for(j in 1:length(m)){
for(k in 1:(r[i]-1)){
m[[cnt]] <- c(m[[j]],i)
cnt <- cnt +1
}
}
}
m
